7
min read

Desarrollamos y validamos dos índices de bienestar de piel no invasivos para salmón usando datos del microbioma y machine learning. Aquí está lo que encontramos:
En la industria acuícola las pérdidas por enfermedades y patógenos ocurren todos los días.
A pesar de que el monitoreo está avanzando, las alternativas no son suficientes. La acuicultura de precisión (sensorizada y con monitoreo constante) tiende a basarse en cámaras y modelos de computer vision. Este monitoreo permite ver cuando los salmones están lesionados o enfermos. El problema es que cuando los signos clínicos aparecen, el sistema ha colapsado, y ya es tarde para evitar mortalidades.
Es por esto que con este trabajo buscamos desarrollar y validar dos índices de bienestar de piel para los salmones que no sean invasivos, y permitan anticipar los riesgos de desarrollo de lesiones. El Gut Wellness Index (GWI), y el Skin Wellness Index (SWI).
El microbioma es la nueva herramienta para esto, en particular el microbioma de la piel y de la mucosa intestinal, el lugar encargado de la absorción de nutrientes y la regulación sistémica del pez.
Obteniendo estas muestras del microbioma podríamos establecer un índice de bienestar de piel del salmón. Un problema importante es que la muestra de microbioma intestinal es destructiva, que requiere eutanasiar al animal para levantar la muestra de mucosa.
Para poder tener una visión general del microbioma del pez, y evitar los manejos innecesarios, planteamos la hipótesis de que se puede usar el microbioma de la piel como proxy de las branquias, y el poro urogenital como proxy del intestino.
Esta investigación tuvo como objetivos:
Validar los proxys,
Desarrollar y comparar modelos de machine learning para medir el estado de la piel, y
Formular dos índices de bienestar no invasivos y prácticos para gestión acuícola.
Codebreaker no limita su I+D a condiciones controladas de laboratorio: colabora con productores, veterinarios y equipos técnicos en centros de cultivo y predios agrícolas, capturando datos reales bajo variabilidad ambiental. – SalmonExpert
171 salmones, 4 muestras cada uno
Para cumplir los objetivos, seleccionamos 171 salmones que fueron categorizados entre individuos sin lesiones en piel (85) y lesionados (86) según signos clínicos de enfermedad.
El muestreo siguió el protocolo estándar y nos apegamos a regulaciones de bienestar animal para asegurar el manejo ético de los peces. En cada salmón utilizamos un hisopo estéril en los segundos arcos branquiales, otro en la piel lateral, un tercer hisopo para el poro urogenital y por último una muestra del intestino distal para la mucosa.
Extrajimos el total del ADN genómico de cada una de las muestras, lo cuantificamos y nos aseguramos de que mantenga una buena calidad. En pocas palabras, secuenciamos y perfilamos los microbiomas.
Codebreaker busca instalar el laboratorio de secuenciación más grande de Chile en Puerto Varas, fortaleciendo su presencia en la región. –Mundo Acuícola
El siguiente paso hacia una métrica específica e intuitiva era hacer un análisis de todos estos datos.
Limpiar los datos y prepararlos para la caracterización fue una de las partes más difíciles según indica Luis León, líder en el apartado de bioinformática: “Tuvimos que dedicar mucho tiempo a la etapa de filtrado y normalización para asegurar que las diferencias que estábamos viendo fueran biológicamente significativas y no simples artefactos técnicos.”
Durante el control de calidad de los datos del muestreo nos dimos cuenta de algo interesante.
A pesar de que la distribución de muestras de los cuatro sitios anatómicos estuvo balanceada, muchas muestras de piel de los peces sanos no tenían suficiente biomasa. Esto puede ser porque los peces sanos producen menos mucosa en su piel, pero es algo que debe estudiarse.
Según Agustín Piña, product manager de Micro-ID™, que se encargó del flujo campo-laboratorio, esta “es una limitación biológica que puede manejarse.” Agustín también indicó que “esto termina enriqueciendo la investigación, porque transparenta dónde el índice funciona mejor y cuáles son sus límites.”
Para mitigar los sesgos en la clasificación por la reducción de muestras de calidad en la piel sana, usamos validación cruzada estratificada y métricas con pesos. Así logramos que el modelo refleje las señales biológicas reales, y en palabras de Luis, con una robustez en los datos que permite que las conclusiones sobre el balance del microbioma sean realmente accionables para la industria.
Diversidad microbiana, una suerte de principio de Ana Karenina
“Todos los microbiomas sanos son parecidos. Cada microbioma enfermo está enfermo a su manera.”
Los análisis de diversidad se dividen en dos: alfa y beta.
El análisis de diversidad alfa mide la variedad y abundancia en el microbioma de un pez. Observamos que el estrés en el microbioma no tiene una sola forma, sino que es muy variado. Por eso decimos que sigue una suerte de principio de Ana Karenina.
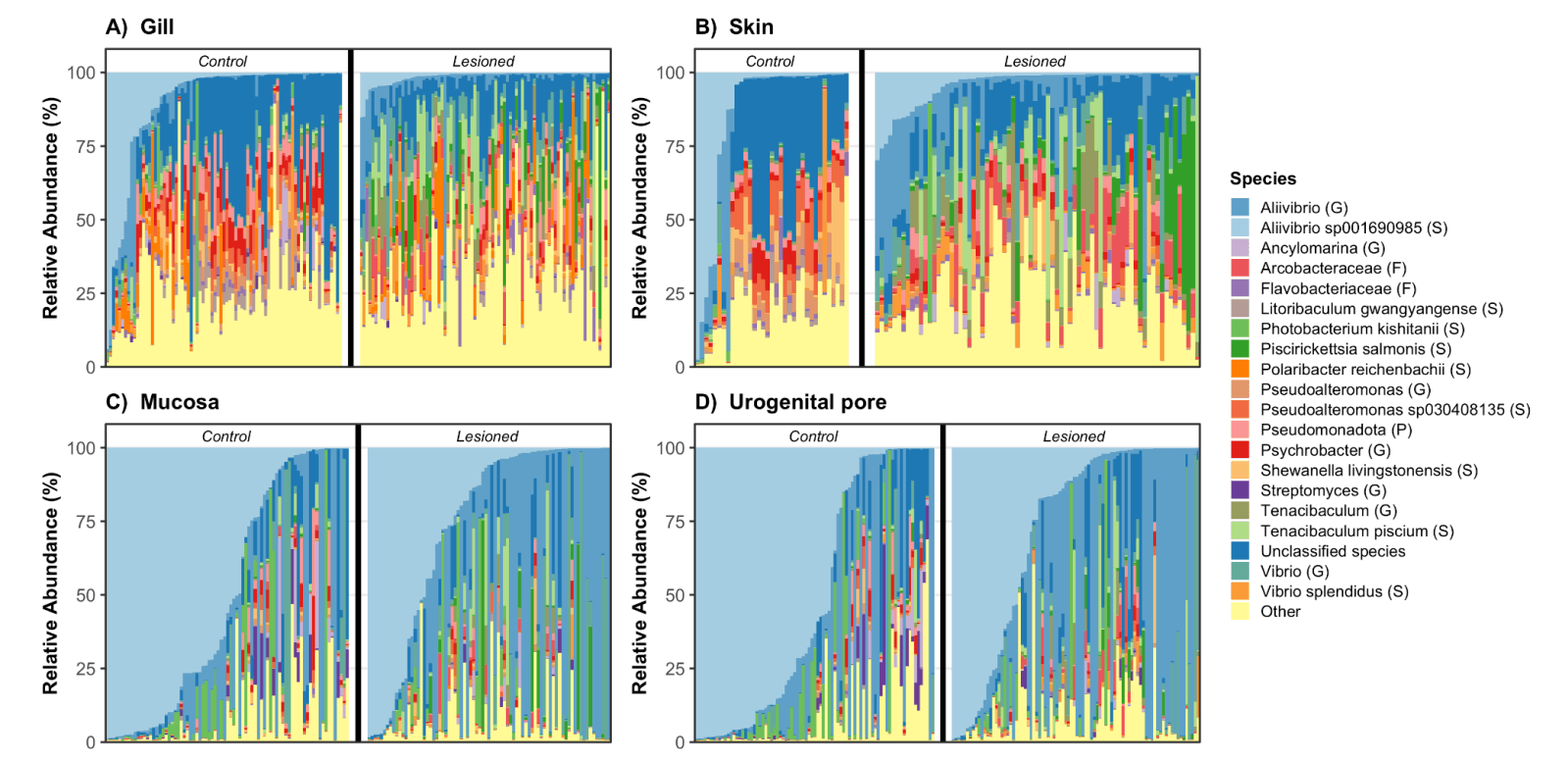
Por otro lado, el análisis de diversidad beta arrojó más información. Este análisis compara la composición del microbioma entre individuos. Para esto usamos PERMANOVA, un test estadístico comúnmente utilizado para evaluar diferencias en microbioma. Con esto confirmamos que un pez enfermo reorganiza su microbioma (p = 0.006).
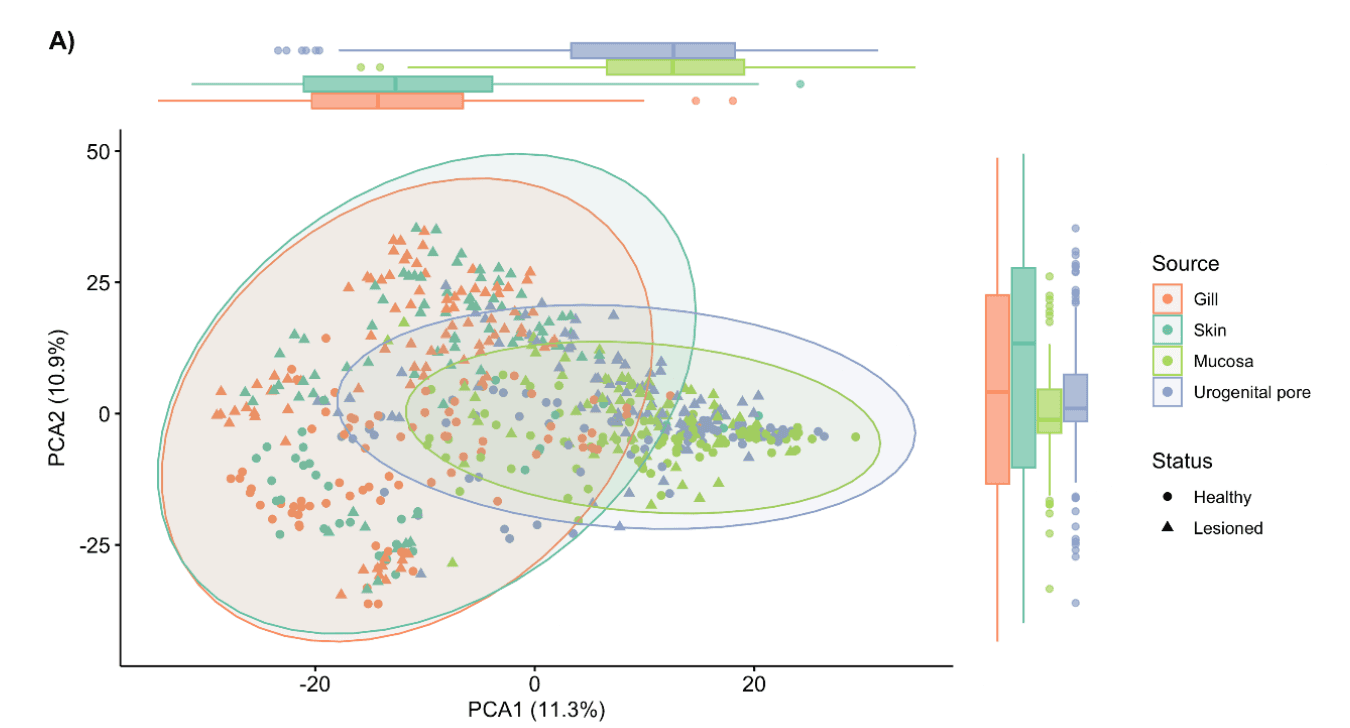
Una vez más apareció el principio de Ana Karenina. Los peces lesionados mostraron una variabilidad en piel mayor que los sanos (p = 0.029), confirmando un quiebre en el balance del microbioma que caracteriza la enfermedad.
Proxys: validados
Sin embargo, por más interesantes que sean estos resultados, un punto a resaltar sacamos de esta investigación fue la validación estadística de los proxys.
Usando tests estadísticos de Procrustes y test de Mantel, confirmamos que el microbioma de la piel y el de las branquias están fuertemente acoplados, al igual que el del poro urogenital y la mucosa intestinal.
Es decir, la piel es un buen proxy de las branquias y el poro urogenital un buen proxy del intestino.
Respecto a los modelos de machine learning, con los datos de los proxys, entrenamos y comparamos siete algoritmos de clasificación distintos.
“Procesamos todo mediante pipelines automatizados en la nube. Esto nos permitió manejar la carga computacional de forma elástica y asegurar que el análisis de cada muestra fuera reproducible” –Luis León, líder en bioinformática en Codebreaker
El objetivo fue predecir si un salmón tiene riesgo de desarrollar lesiones en piel en base a su microbioma.
Después de la comparación de modelos, resultó que el óptimo es la regresión logística.
El área bajo la curva (AUC) mide qué tan bien un modelo distingue entre distintos grupos y considera una puntuación de 1.0 como perfecta y 0.5 como azar. Para la piel, el modelo alcanzó un AUC de 0.967, y para el poro urogenital, se obtuvo un AUC de 0.869.
Con esto, pudimos formular los índices a los que apuntábamos.
El Skin Wellness Index (SW), basado en la piel, y el Gut Wellness Index (GWS), basado en el poro urogenital. Ambos entregan un valor continuo entre 0 y 1, donde 0 representa el microbioma de un pez que no desarrolla lesiones y 1 un pez cuyo microbioma es de uno lesionado.
Lo más interesante es la zona de transición: peces cuyos puntajes caen entre 0.5 y 0.8, con perfiles microbianos de un individuo que desarrolla lesiones, pero que aún no han mostrado signos clínicos visibles. Esa zona es donde reside el potencial diagnóstico preventivo, y el punto más relevante de este estudio, porque permite anticipar medidas productivas para evitar el colapso sanitario del centro
Cuando el microbioma se desvía de la línea estándar de un pez que no desarrolla lesiones, podemos alertar de un riesgo biológico inminente para el cultivo.
Ahí está la capacidad de evitar el colapso del sistema, y por consiguiente la enfermedad antes de que ocurra.
Limitaciones del estudio
Como todo artículo científico, esta investigación tiene ciertas limitaciones que son desafíos a futuro.
Este estudio está diseñado en que la ground truth (información verificada) para el modelo de machine learning es en base a signos clínicos visuales. Esto significa que arroja los mismos resultados que los signos clínicos pero a través de una métrica cuantitativa estandarizada.
Esto quiere decir que nuestro modelo, técnicamente y por diseño, no puede detectar la enfermedad antes de que aparezcan los signos clínicos, sino que detecta cuando se pierde el balance del microbioma.
Para conseguir detección temprana precisa, se tendrían que realizar estudios longitudinales con muestreos antes de una enfermedad. A pesar de esto, haber identificado una "zona de transición" en que los perfiles del microbioma divergen de la línea sana indica que existen estados intermedios y que futuras investigaciones podrían determinar si esos estados preceden la enfermedad.
En palabras de Agustín, “La pregunta grande es si el indicador puede detectar cambios antes de que aparezcan los signos clínicos, y para eso necesitas muestreos seriados en el tiempo.”
Por otro lado, todos los peces tienen procedencia de una misma cohorte del mismo centro. El product manager de Micro-ID™ indicó la importancia de la validación multi-centro. “Todos los peces vienen de una misma cohorte en un solo centro, y sabemos que el microbioma basal cambia según genética, agua, dieta, temperatura. Los umbrales del indicador probablemente necesitan calibrarse para cada contexto productivo.”
A pesar de esto, las relaciones de proxy establecidas y el rendimiento en la clasificación es un avance muy fuerte para una acuicultura proactiva.
Conclusión
Con este estudio demostramos que los perfiles del microbioma de los salmones tienen información sobre el estado de bienestar de la piel y que puede ser obtenido con muestreos no invasivos. Además de esta información se puede traducir a puntajes cuantitativos de bienestar a través de machine learning.
Los indicadores de bienestar de piel desarrollados aquí representan, a nuestro conocimiento, los primeros índices basados en el microbioma con múltiples parámetros de la industria acuícola.
A pesar de que aún se requiere validación de estudios longitudinales, los marcos de trabajo que desarrollamos sientan las bases de una transición en la industria. Pasando de reaccionar a eventos sanitarios a gestionar la salud a través de información del microbioma. Estos avances indican un potencial para reducir la dependencia a antibióticos y mejorar el bienestar de la producción.
For more information
Contact
+56995114707
dna@codebreaker.bio
Klenner 299, of. Patagonia hub tech, Puerto Varas
